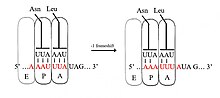
미끄러운 순서
Slippery sequence미끄러운 시퀀스는 리보솜 프레임 쉬핑 속도와 기회를 제어하는 코돈 뉴클레오티드 시퀀스(일반적으로 UUUAAC)의 작은 섹션이다.미끄러운 시퀀스는 리보솜의 빠른 전달을 유발하며, 이는 다시 리보솜을 "슬립"하게 할 수 있다.이를 통해 tRNA가 안티코돈과 페어링된 후 1base(-1)만큼 이동하여 판독 프레임을 변경할 수 있다.[2][3][4][5][6]이러한 시퀀스에 의해 트리거된 -1 프레임시프트는 프로그래밍된 -1 리보솜 프레임시프트다.스페이서 영역, RNA 이차 구조 뒤에 온다.그러한 순서는 바이러스 다단백질에서 흔히 볼 수 있다.[1]
프레임시프트는 비틀거리는 페어링으로 인해 발생한다.하류에 있는 2차 구조물의 깁스 자유 에너지는 프레임시프트가 얼마나 자주 일어나는지 힌트를 준다.[7]mRNA 분자의 긴장도 작용한다.[8]동물 바이러스에서 발견된 미끄러운 결과의 목록은 Huang 등으로부터 구할 수 있다.[9]
2베이스 슬립(-2프레임시프트)을 일으키는 미끄러운 시퀀스는 HIV UUUUUUUA 시퀀스로 구성되었다.[8]
참고 항목
참조
- ^ a b Jacks T, Madhani HD, Masiarz FR, Varmus HE (November 1988). "Signals for ribosomal frameshifting in the Rous sarcoma virus gag-pol region". Cell. 55 (3): 447–58. doi:10.1016/0092-8674(88)90031-1. PMC 7133365. PMID 2846182. S2CID 25672863.
- ^ Green L, Kim CH, Bustamante C, Tinoco I (January 2008). "Characterization of the mechanical unfolding of RNA pseudoknots". Journal of Molecular Biology. 375 (2): 511–28. doi:10.1016/j.jmb.2007.05.058. PMC 7094456. PMID 18021801.
- ^ Yu CH, Noteborn MH, Olsthoorn RC (December 2010). "Stimulation of ribosomal frameshifting by antisense LNA". Nucleic Acids Research. 38 (22): 8277–83. doi:10.1093/nar/gkq650. PMC 3001050. PMID 20693527.
- ^ "Dr Ian Brierley Research description". Department of Pathology, University of Cambridge. Archived from the original on 2013-10-02. Retrieved 2013-07-28.
- ^ "Molecular Biology: Frameshifting occurs at slippery sequences". Molecularstudy.blogspot.com. 2012-10-16. Retrieved 2013-07-28.
- ^ Farabaugh PJ, Björk GR (March 1999). "How translational accuracy influences reading frame maintenance". The EMBO Journal. 18 (6): 1427–34. doi:10.1093/emboj/18.6.1427. PMC 1171232. PMID 10075915.
- ^ Cao S, Chen SJ (March 2008). "Predicting ribosomal frameshifting efficiency". Physical Biology. 5 (1): 016002. Bibcode:2008PhBio...5a6002C. doi:10.1088/1478-3975/5/1/016002. PMC 2442619. PMID 18367782.
- ^ a b Lin Z, Gilbert RJ, Brierley I (September 2012). "Spacer-length dependence of programmed -1 or -2 ribosomal frameshifting on a U6A heptamer supports a role for messenger RNA (mRNA) tension in frameshifting". Nucleic Acids Research. 40 (17): 8674–89. doi:10.1093/nar/gks629. PMC 3458567. PMID 22743270.
- ^ Huang X, Cheng Q, Du Z (2013). "A genome-wide analysis of RNA pseudoknots that stimulate efficient -1 ribosomal frameshifting or readthrough in animal viruses". BioMed Research International. 2013: 984028. doi:10.1155/2013/984028. PMC 3835772. PMID 24298557.
외부 링크
- 유사분해효소
- 리코드
- 프레임 쉬핑, + 미국 국립 의학 도서관의 리보솜(MesH)
- Wise2 - DNA 서열에 맞춰 단백질을 정렬하여 프레임 변형 및 인트론 가능
- FastY - DNA 염기서열을 단백질 염기서열 데이터베이스와 비교하여 틈새 및 프레임 변형 허용
- 경로 - 두 개의 프레임시프트 단백질을 비교하는 도구(백번역 원리)
- Recode2 - 프로그래밍된 Translational frameshift를 필요로 하는 유전자를 포함한 재코딩된 유전자의 데이터베이스.
- Rfam의 Coronavirus frameshifting 자극 요소 페이지