바이오슬랙스
BioSLAX BioSLAX에서 실행되는 다양한 바이오 앱 | |
| 개발자 | 싱가포르 국립 대학교 바이오 인포매틱스 센터 (리소스) 마르크 데 실바 임관시옹 탄틴위 |
|---|---|
| OS 패밀리 | Linux (Unix라이크) |
| 동작 상태 | 현재의 |
| 소스 모델 | 오픈 소스 |
| 최신 릴리즈 | v7.5 / 2009년2월 5일, 전( |
| 커널 타입 | 모노리식 커널 |
| 면허증. | 여러가지 |
| 공식 웹사이트 | www.bioslax.com |
BioSLAX는 300개 이상의 바이오 인포매틱스 도구와 애플리케이션 스위트로 구성된 라이브 CD/Live DVD/Live USB입니다.싱가포르 국립 생명과학연구소(LSI)의 생물정보학 리소스 유닛(Bioth Informatics Resource Unit)에 의해 출시되었으며 CD/DVD 또는 USB 부팅 옵션을 사용할 수 있으며 Linux 운영체제(OS)의 압축된 슬랙웨어 플레이버를 실행하는 모든 PC에서 부팅할 수 있습니다.슬랙스는 체코에서 Linux Live Scripts를 사용하여 Tomash Matjjichek에 의해 만들어졌습니다.BioSLAX 파생상품은 Mark De Silva, Lim Kuan Siong 및 Tan Tin Wee에 의해 개발되었습니다.
BioSLAX는 2006년 4월에 NUS 생명과학 커리큘럼에 처음 공개되었습니다.
역사
2003년 1월, APBioNet은 IDRC(캐나다)의 PAN(Pan Asia Networking) 프로그램으로부터 APBioBox를 구축하기 위한 노력의 일환으로 그리드 컴퓨팅 소프트웨어를 사용하여 일반적으로 사용되는 생물 정보 애플리케이션과 패키지의 APBioBox를 구축하기 위한 연구 보조금을 받았다.선택한 플랫폼은 당시 어디서나 사용 가능했던 Redhat Linux였습니다.같은 해 3월 APBioNet은 AIPS(Industry Partnership Scheme)를 출시하고 Sun Microsystems와 협력하여 Solaris 플랫폼용 BioBox를 구축했습니다.6개월 후 APBioBox와 Sun의 바이오박스 베타 버전이 출시되었으며, 현재는 Bio-Cluster Grid로 불리고 있습니다.패키지에는 [1]각각 Globus Grid Toolkit 버전 2.0과 Sun Grid Engine이 포함되어 있습니다.
2003년 12월 4일 현재 APBioBox(Redhat Linux) 및 BioCluster Grid(Sun Solaris)라는 이름의 바이오박스 소프트웨어 패키지가 필리핀 과학기술부(DOST)의 ASTI(Advanced Science and Technology Institute)에서 실시된 바이오정보학 워크숍에서 현장 테스트를 받았습니다.검색 위원회(NRCP)를 참조하십시오.10대의 펜티엄 머신과 2대의 Sun 서버가 APBioGrid에 성공적으로 도입되었습니다.이 워크숍과 테스트한 소프트웨어는 Sun Microsystems가 후원하고 IDRC가 부분적으로 자금을 지원했습니다.
2004년 7월 Derek Kiong 박사는 2004년 9월까지 NUS의 시스템 과학 연구소(ISS)가 주최한 워크숍에서 Knopix가 A/Profess Tan Tin Wee에게 안정적이고 강력한 소형 Unix(Debian 기반) 플랫폼이라고 소개하여 Knoppix를 만들었습니다.ul을 시제품 APBioKnoppix에 적용하기 위해 [2]NUS 생화학부의 LSM2104 모듈의 실제 과정을 위한 프로젝트로 사용합니다.이후 Knoppix 4.02를 기반으로 업그레이드되어 APBioKnoppix2로 [3]출시되었습니다.APBioKnoppix는 널리 사용되었지만 쉽게 확장할 수 없는 것으로 나타났습니다.리마스터링 전에 모든 애플리케이션을 배치해야 했기 때문에 배포가 매우 유연하지 못했습니다.
2005년 6월, 생명과학연구소(LSI)의 생물정보학 자원 유닛의 Mark De Silva는 단일 모듈을 추가하여 동일한 베이스 시스템을 효과적으로 사용할 수 있고 다양한 도구 또는 변경을 상단 베이스에 쉽게 포함할 수 있는 모듈식 시스템 때문에 Slax를 새로운 바이오 기반 라이브 CD의 베이스로 사용할 것을 제안했다.모든 응용 프로그램 파일 또는 변경.이를 통해 Knoppix의 경우처럼 새로운 소프트웨어나 변경이 발생할 때마다 시스템 전체를 재기동할 필요가 없어졌습니다.
2006년 4월까지 BioSLAX의 첫 번째 버전은 여러 에디션과 함께 출시되었습니다.
- Standard User Edition (530 MB)
- Developer Edition (700 MB)
- Sever Edition (470 MB)
BioSLAX는 이후 생명과학 커리큘럼의 NUS 내 생물정보학 교육 모듈뿐만 아니라 아시아 태평양 생물정보학 네트워크(APBioNet)의 산하에 조직된 여러 행사에 사용되었다.APBioNet은 ISCB(International Society for Computational Biology)의 지역 계열사입니다.NUS와 APBioNet을 모두 지원하도록 맞춤형 버전이 구축되었습니다.
2007년 8월에는 APBioNet과 협력하여 베트남 하노이 바이오아카데미 바이오정보학 자원 서버인 바이오IBT에 베트남 바이오정보학 자원 노드를 설정하기 위해 맞춤형 BioSLAX가 사용되었습니다.Bio-IBT 노드는 다음을 제공합니다.
- 생물 데이터베이스의 Bio Mirrors 저장소
- NCBI BLOAST 미러 리소스
- EBI EMBOSS 응용 프로그램에 대한 웹 액세스
- CLUSTALW 다중 시퀀스 정렬에 대한 웹 액세스
- T-Coffee 다중 시퀀스 정렬에 대한 웹 액세스
- PHYLIP 계통발생학적 추론 패키지에 대한 웹 액세스
- Sequence Manipulation Suite, SMS2에 대한 웹 액세스
서버에 SSH로 액세스 할 수 있는 유저는, 커맨드 라인 베이스의 바이오/라이프 사이언스 애플리케이션에도 액세스 할 수 있었습니다.
전체 프로젝트는 2007년 8월 20일부터 31일까지 베트남에서 개최된 제1회 유네스코-IUBMB-FAOBMB-APBioNet 생물정보학 워크숍과 공동으로 수행되었으며, 2007년 제6회 생물정보학 국제회의(InCoB) 위성 행사이다.
APBioNet의 국제기구에 배치된 BioSLAX의 일부 버전에는 IP를 동적으로 생성된 apbionet.org 도메인 이름에 매핑할 수 있는 작은 도구가 장착되어 각 머신에 Fully Qualified Domain Name(FQDN; 완전 수식 도메인 이름)과 인터넷상의 [citation needed]존재감을 부여합니다.
모듈러성
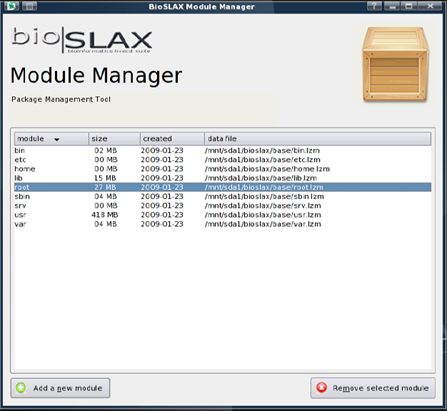
Slax는 기본 Linux OS 위에 "애플리케이션 모듈"을 겹쳐서 작동하기 때문에 전체 배포판을 모듈화했습니다.시스템이 이미 가동되고 있는 동안에도 이러한 모듈을 도입하는 기능이 추가되어 Slax를 사용하는 것이 더욱 매력적이었습니다.GUI 기반의 "BioSLAX Module Manager"를 탑재함으로써 모듈을 동적으로 추가하거나 분리하는 프로세스가 더욱 쉬워졌습니다.
사용자는 소프트웨어 또는 새 버전의 업데이트를 테스트하고 필요에 따라 이전 버전으로 "롤백"할 수 있었습니다.SLAX/BioSLAX를 USB 드라이브와 같은 쓰기 가능한 미디어에 설치하는 경우 특히 효과적이었습니다.
버전
현재까지 BioSLAX에는 Slax 5 기반 BioSLAX 5.x와 Slax 6 기반 BioSLAX 7.x의 두 가지 버전이 있습니다.BioSLAX 5.x는 Slax 5의 버전 번호를 따랐지만, BioSLAX 7은 Slax의 기반 버전보다 한 단계 높은 새로운 버전 번호를 채택했다.최신 버전은 BioSLAX [4]웹사이트에서 다운로드할 수 있습니다.
BioSLAX 5.x
BioSLAX 5.x는 주로 Slax 5.1.8 버전에 기반을 두고 있으며, 2.6 Linux 커널과 KDE 3.4의 이전 버전을 실행하며 unionf를 포함하고 있다.
BioSLAX 5.x 에디션
표준 사용자 에디션
이 에디션은 KDE X Window GUI를 실행하며 모든 도구와 응용 프로그램 스위트와 함께 제공되지만 컴파일러 도구나 Linux 커널 소스 코드 및 헤더는 포함되지 않습니다.이 기능은 주로 도구 및 애플리케이션 스위트만 사용해야 하는 사용자에게 적합합니다.크기가 매우 작기 때문에 다운로드가 쉽고 특히 인터넷 대역폭이 문제가 되는 지역에서 편리합니다.
개발자 에디션
이 에디션은 KDE X Window GUI를 실행하며 모든 도구와 응용 프로그램 스위트와 함께 제공되며, 또한 Linux 커널 소스 코드와 헤더를 포함한 완전한 개발 및 컴파일러 도구 세트를 포함합니다.이 에디션은 다양한 툴과 어플리케이션을 사용하는 것 외에 새로운 어플리케이션을 컴파일하거나 BioSLAX용 어플리케이션모듈을 새로 만들고 싶은 파워 유저에게 적합합니다.
서버 에디션
이 에디션에는 X Window GUI, 컴파일 도구, Linux 커널 소스 또는 커널 헤더는 포함되어 있지 않습니다.주로 리모트 서버로서 사용하는 것을 목적으로 하고 있습니다.사용자는 SSH를 사용하여 명령줄 어플리케이션을 사용하거나 웹을 통해 서버에 접속하여 일반적인 바이오 어플리케이션의 웹 기반 포털에 액세스해야 합니다.
NUS LSM 에디션
이 에디션은 NUS 생명과학 커리큘럼에서 생물정보학 교육을 위해 사용하도록 맞춤화된 Developer Edition입니다.
타베르나 에디션
이 에디션은 TaveRNA가 포함된 Developer Edition입니다.TaveRNA 프로젝트는 워크플로우와 분산 컴퓨팅 기술을 쉽게 사용할 수 있도록 언어와 소프트웨어 도구를 제공하는 것을 목표로 하고 있습니다.
BioSLAX 7.x
BioSLAX 7.x는 Slax 6을 기반으로 하며 2.6 Linux 커널 KDE 3.5의 최신 릴리스와 aufs 및 lzma 압축을 사용합니다.가장 큰 변화는 이 버전을 클라이언트 또는 서버로 사용하는 것입니다.배포도 CD에서 DVD로 이동했기 때문에 이전에는 공간 문제로 인해 버전 5.x에서 제외되었던 더 많은 애플리케이션을 도입할 수 있게 되었습니다.FAT 또는 EXT 형식의 USB 드라이브에서 부팅하는 기능도 Slax 6에서 도입되었습니다.따라서 BioSLAX 7.x 버전에서는 CD/DVD에서 사용할 수 없는 (재기입이 불가능하기 때문에) 영속적인 파일 처리를 효과적으로 가능하게 합니다.
바이오슬랙스 8
7.x 이후의 BioSLAX 버전은 베이스 디스트리뷰션(슬랙스)의 개발자 Tomāsh Matíjichek이 가족의 약속 때문에 새로운 버전의 진행을 거부하여 지연되었습니다.그러나 그가 앞으로 나아가지 않은 주된 이유는 사용자가 별도의 패치를 적용하지 않고 기본적으로 Squash FS와 LZMA가 Linux 커널에 통합되기를 기다렸기 때문입니다.커널 2.6.38을 기준으로 통합이 최종적으로 완료되었으며, 이로 인해 Tomash Matjjichek은 Slax의 새로운 버전을 검토하게 되었고, 따라서 향후 몇 개월 내에 새로운 버전의 BioSLAX가 출시될 것입니다.자신의 [needs update?]블로그에서 슬랙스의 새로운 버전에 대한 그의 생각을 따라 할 수 있다.
특징들
표준 도구
Bio SLAX는 Linux Slackware 12.1 운영체제에 다양한 무선카드 지원 등 다양한 네트워크 어댑터용 드라이버 업데이트를 탑재하고 있습니다.또한 다음과 같은 유용한 기본 도구와 응용 프로그램이 많이 있습니다.
- PERL(BioPerl 모듈 포함)
- PHP
- 아파치 2
- MySQL
- OpenOffice.org
- KPDF 리더
- 모질라 파이어폭스
- 모질라 썬더버드
- gFTP
- ProFTPd
- OpenSSH
- 코페테 인스턴트 메신저
- VNC 뷰어
- 리모트 데스크톱 서비스
바이오 인포매틱스 도구
생물정보학 도구와 애플리케이션은 세 가지 주요 범주로 세분된다.
콘솔 앱
데스크톱 애플리케이션
- 행동하다
- 아르테미스
- ClusteralX(GUI 기반 ClusteralW)
- 쟈리그너
- 잘뷰
- jEMBOSS(Java EMBOSS Suite)
- 즈몰
- NJPlot
- 파이몰
- 읽기 SEQ
- 트리뷰
- Weka(기계학습)
웹 어플리케이션
하드 디스크에 설치
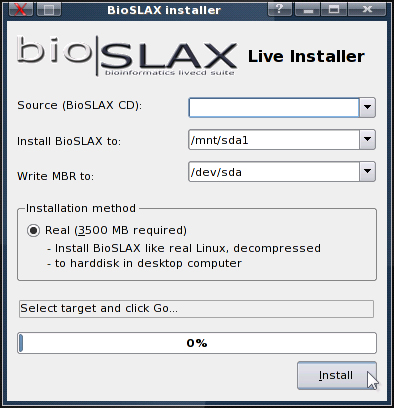
슬랙스 기반 디스트리뷰션의 가장 흥미로운 기능 중 하나는 라이브 OS를 모든 PC의 하드 드라이브에 설치되어 있는 완전한 Linux 시스템으로 쉽게 변환할 수 있다는 것입니다.이것에 의해, 약 3.5 의 시간이 소요됩니다.GB의 공간
KDE Kommander 툴킷으로 작성된 "BioSLAX Installer"라는 툴이 제공되어 사용자는 라이브 OS를 완전한 Linux 설치로 쉽게 변환할 수 있습니다.모듈을 사용하여 배포를 커스터마이즈한 후 instra를 사용하면 완전히 설치된 맞춤형 클라이언트를 신속하게 도입할 수 있습니다.
장래의 계획
Bio SLAX 업데이트
BioSLAX는 새로운 Slackware(또는 Slax) 버전이 출시되면 업데이트됩니다.툴과 애플리케이션 스위트도 중요한 변경이 있는지 감시하고 필요에 따라 업그레이드합니다.일부 도구는 동일한 작업을 수행할 수 있지만 기능이 추가되고 효율성이 향상된 다른 도구에 자리를 내주기 위해 제거될 수 있습니다.예를 들어 ReadSeq, Primer3, Genesplicer에 대한 포털이 준비되고 있는 등 더 많은 웹 기반 포털이 검토되고 있다.
그리드 도입
개발자들은 또한 다양한 그리드 컴퓨팅 플랫폼을 BioSLAX와 통합하는 것을 검토하고 있었습니다.BioSLAX는 CD/DVD/USB에서 즉시 부팅할 수 있기 때문에 신속하게 도입 가능한 그리드 대응 운영체제로 사용할 수 있습니다.그러한 그리드 플랫폼 중 하나가 Univa 그리드 플랫폼입니다.Univa Grid MP 에이전트를 사용하면 GridAsia 2009년 Tan Tin Wee의 강연에서 BioSLAX로 모듈화된 에이전트를 사용하여 모든 위치에서 슬레이브 노드로 머신을 다른 위치에 있는 마스터 노드로 그리딩하여 효과적으로 "글로벌 그리드"를 구축할 수 있음을 알 수 있습니다.
클라우드의 BioSLAX
개념 실증 노력의 일환으로 개발자는 VMWare의 ESXi와 Citrix Xen의 하이퍼바이저를 모두 사용하여 BioSLAX를 리소스 풀에 인스턴스로 도입하는 데 성공했습니다.그 목적은 학생과 스탭이 임의의 수의 BioSLAX 서버를 연구 및 교육용으로 동적으로 인스턴스화할 수 있는 "BioSLAX CLUAD"를 효과적으로 구축하는 것이었습니다(학생이 X-Win32, VNC, Exceed, No Machine NX 등의 적절한 X Wind 클라이언트를 통해 서버에 접속하도록 함으로써 바이오 인포매틱스 실습 실시).UD Grid mpagent와 함께 사용하면 큰 작업을 처리하기 위한 클러스터를 형성할 수 있습니다.
개념 실증(Proof-of-Concept)은 NUS의 생명과학 커리큘럼 연구 및 교육에 매우 성공적으로 도입되었으며, 2011년에는 VMWare의 vSphere 및 Citrix Xen 서버 모두에서 다수의 BioSLAX 클라우드 인스턴스가 APBioNet 프로젝트인 BioDB100에 사용되었습니다.백엔드 제어 및 자동화는 Mark De Silva 씨가 vSphere 및 Xen용 다양한 API를 사용하여 생성하고 구현했습니다.
개발자들은 또한 2009년부터 2010년까지 아마존 EC2에 유사한 BioSLAX 클라우드 이미지를 도입하기 위해 아마존과 협의 중이었고, 연구 및 교육 머신의 일부를 아마존에 넘겨 하드웨어 비용을 절감하고자 했습니다.그러나 Amazon이 BioSLAX 이미지를 클라우드에서 실행하기 위해 필요한 완전한 하드웨어 가상화를 지원하지 않을 것이 분명해지자 논의가 무산되었습니다.실제로 Citrix Xen 하이퍼바이저를 사용하는 대부분의 상용 클라우드 프로바이더는 파라 가상화만 지원합니다.이러한 엔티티의 사고방식이 바뀔 때까지 완전한 하드웨어 가상화를 위해 구성된 Citrix Xen 하이퍼바이저를 실행하는 프라이빗 클라우드 또는 VMware vSphere 클라우드만이 BioSLAX를 실행할 수 있는 유일한 클라우드입니다.