세포의 모델
Cellular model이 기사는 문제에 대한 전문가에서 관심이 필요하다구체적인 문제:기술 재료의 큰 덩어리 여기에 컨텍스트에 위치하지 않다.이 태그를, WikiProject고 부탁을 결부시키는 것이 좋습니다. |
생물학적 세포의 여러가지 양상에silico의 연구가 적용되는 세포 모델은 수학적 모델,.
시스템 생물학과 수학적 생물학의 모델 개발하는 것은 과제이다.생물학적인 큰 데이터 양의 컴퓨터 모델링의 목표를 통합 조직할 효율적인 알고리즘이나 자료 구조, 시각화와 의사 소통 도구 개발을 포함한다.그것은 대사 물질과 신진대사, 신호 전달 경로와 유전자 조절하는 망을 차지하고 있어 효소의 네트워크와 같은 휴대 전화 서브 시스템의 컴퓨터 시뮬레이션의 사용을 포함한다.
개요
진핵 세포 주기는 매우 복잡하고 그것의 잘못된 조절이 암을 유발하기 때문에 가장 많이 연구된 주제 중 하나이다.이것은 간단한 미적분을 다루지만 유효한 결과를 제공하므로 수학 모델의 좋은 예가 될 수 있다.두 연구 그룹이[1][2] 여러 유기체를 시뮬레이션하는 세포 주기의 여러 모델을 만들어냈다.그들은 최근 파라미터의 값에 따라 특정 진핵생물을 나타낼 수 있는 일반적인 진핵생물 세포주기 모델을 생산했다. 이는 개별 세포주기의 특이성이 단백질 농도와 친화력이 다른 반면 기초 메커니즘은 보존된다는 것을 보여준다(Cikasz-Nagy et al, 2).006).
상미분방정식의 시스템에 의해 이 모델들은 하나의 전형적인 세포 안에서 단백질의 시간 변화를 보여준다; 이 모델의 유형은 결정론적 과정이라고 불린다. (여기서 세포 집단에서 단백질 농도의 통계적 분포를 설명하는 모델은 확률적 과정이라고 불린다.)
이러한 방정식을 얻기 위해 반복적인 일련의 단계가 이루어져야 한다: 먼저 여러 모델과 관찰이 합의도를 형성하기 위해 결합되고 적절한 운동 법칙이 화학량학 반응을 위한 속도 운동학, 효소 기질 반응을 위한 미카엘리스 멘텐 운동학 그리고 골드와 같은 미분 방정식을 쓰기 위해 선택된다.초감응성 전사 인자에 대한 beter-Koshland kynetics, 이후 방정식의 매개변수(속도 상수, 효소 효율성 계수 및 Michaelis 상수)를 일치시키기 위해 적합해야 한다. 적합할 수 없는 경우 운동 방정식이 수정되고 가능하지 않은 경우 배선 다이어그램이 수정된다.매개 변수는 단백질 반감기와 세포 크기와 같은 야생 유형 및 돌연변이 관측치를 사용하여 적합되고 검증됩니다.
매개변수를 맞추려면 미분 방정식을 연구해야 합니다.이는 시뮬레이션 또는 분석에 의해 수행될 수 있습니다.
시뮬레이션에서 시작 벡터(변수 값의 리스트)가 주어졌을 때, 각 시간 프레임에서의 방정식을 소량씩 풀어서 시스템의 진행을 계산한다.
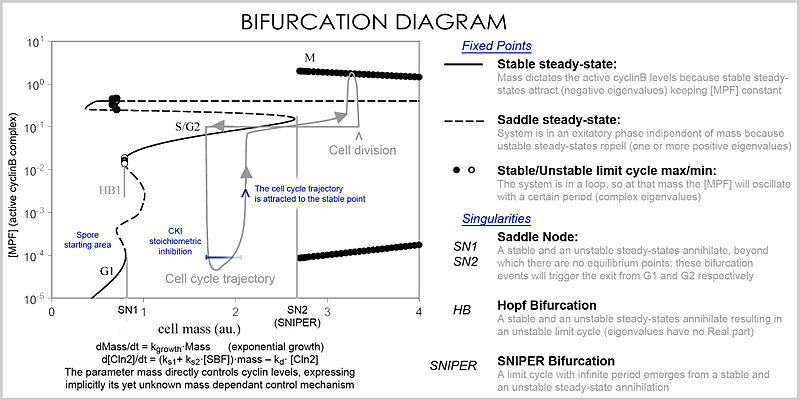
분석에서 방정식의 특성은 파라미터와 변수의 값에 따른 시스템의 동작을 조사하기 위해 사용됩니다.미분방정식 시스템은 벡터장으로 표현될 수 있으며, 여기서 각 벡터는 궤적(시뮬레이션)이 어디로 얼마나 빠르게 향하고 있는지를 결정하는 변화(두 개 이상의 단백질 농도)를 기술한다.벡터 필드는 여러 특별한 점을 가질 수 있다: 모든 방향으로 끌어당기는 싱크라고 불리는 안정점, 불안정한 점, 반발하는 소스 또는 안장점(특정 값에서 벗어나도록 강제) 및 한계 사이클, 닫힌 궤적(농도를 진동시키는) 몇 가지 궤적을 향해 나선형으로 움직입니다.
많은 변수와 매개변수를 처리할 수 있는 더 나은 표현은 분기도(bifurcation 이론)라고 불린다: 매개변수의 특정 값(예를 들어 질량)에 이러한 특별한 정상 상태 점의 존재는 점으로 표현되며 매개변수가 특정 값을 통과하면, 비푸라고 하는 질적 변화가 일어난다.단백질 농도에 대한 심각한 결과를 수반하는 공간의 성질이 변화한다: 세포 사이클은 질량이 안정된 지점을 통해 사이클린 레벨을 제어하는 단계(부분적으로 G1과 G2에 대응)와 농도가 독립적으로 변화하는 단계(S와 M 단계)를 가진다.그러나 일단 위상이 bi에서 변화했다.퍼케이션 이벤트(셀 사이클 체크포인트), 시스템은 이전 수준으로 돌아갈 수 없다. 왜냐하면 현재 질량에서는 벡터장이 크게 다르고 질량이 분기 이벤트를 통해 역전될 수 없기 때문이다. 따라서 체크포인트는 되돌릴 수 없다.특히 S와 M 체크포인트는 Hopf 분기 및 무한 주기 분기라고 하는 특수 분기로 조절된다.
분자 수준 시뮬레이션
Cell[3] Collective는 동적 생물학적 데이터를 저장하고, 계산 모델을 구축하고, 모델을 자극하고, 파괴하고, 재현할 수 있는 모델링 소프트웨어입니다.이 개발은 컴퓨터 생물학 분야의 연구자인 토마스 헬리카르가 [4]주도하고 있다.이것은 생물학자, 컴퓨터 생물학을 배우는 학생, 생명과학을 가르치는 데 초점을 맞춘 교사 및 생명과학 분야의 연구자들을 위해 설계되었습니다.수학과 컴퓨터 과학의 복잡성은 백엔드에 내장되어 있어 생물종을 모델링하는 방법을 배울 수 있지만, 복잡한 수학 방정식, 알고리즘, 프로그래밍은 필요하지 않기 때문에 모델 구축을 방해하지 않습니다.
Cell Collective의 수학적 프레임워크는 각 노드의 규제 메커니즘이 논리 함수로 기술되는 공통 질적(이산) 모델링 기술에 기초하고 있다.
2012년 7월호 Cell에서 스탠포드의 Markus Convert가 이끄는 팀은 지금까지 가장 완벽한 세포 계산 모델을 발표했습니다.대략 500-gene Mycoplasma generalium의 모델은 900개 이상의 소스로부터 작업을 통합하는 28개의 알고리즘에 독립적인 구성 요소를 포함하고 있다.그것은 유기체의 완전한 게놈, 전사체, 프로테옴, 대사체의 상호작용을 설명하며,[7][8] 이 분야에 있어 중요한 발전을 나타낸다.
세포 주기 과정을 모델링하려는 대부분의 시도는 세포 주기의 S, M, G1 및 G2 단계에 해당하는 몇 가지 사이클린 및 사이클린 의존 키나제 분자를 포함한 많은 다른 화학 물질의 광범위하고 복잡한 분자 상호작용에 초점을 맞췄다.2014년 발행된 PLOS 컴퓨터 생물학 기사에서 옥스포드 대학, 버지니아 공대 및 Institut de Génétique et Dévelopment de Rennes의 공동 연구진은 단 한 번의 사이클린/CDK 상호작용을 사용하여 세포 주기의 단순화된 모델을 제작했다.이 모델은 하나의 상호작용만을 조절하고 조작함으로써 세포분열을 완전히 기능적으로 제어할 수 있는 능력을 보여주었으며, 심지어 [9]CDK 농도의 변화를 통해 단계를 생략할 수 있게 했다.이 모델은 한 화학 물질의 비교적 단순한 상호작용이 세포 분열의 세포 수준 모델로 어떻게 변환되는지를 이해하는 데 도움을 줄 수 있다.
프로젝트
여러 프로젝트가 [10]진행 중입니다.
- 사이토솔브
- 합성 셀
- 카리오테 - 인디애나 대학교
- E-Cell 프로젝트
- 버추얼 셀 - 코네티컷 대학교 헬스 센터
- 실리콘 셀
- 홀셀 - 스탠포드 대학교
- MCell - 국립생물시스템멀티스케일모델링센터(MMBioS)
「 」를 참조해 주세요.
- 생체 데이터 시각화
- 분기 이론의 생물학적 응용
- 분자 모델링 소프트웨어
- 멤브레인 컴퓨팅은 특정 세포막을 모델링하는 작업입니다.
- 세포 사이클에서의 생화학 스위치
- 토미타 마사루
레퍼런스
- ^ "The JJ Tyson Lab". Virginia Tech. Retrieved 2011-07-20.
- ^ "The Molecular Network Dynamics Research Group". Budapest University of Technology and Economics. Archived from the original on 2019-10-30. Retrieved 2011-07-20.
- ^ "Interactive Modeling of Biological Networks".
- ^ "Helikar Lab - Members". Archived from the original on 2019-10-19. Retrieved 2016-02-15.
- ^ Morris MK, Saez-Rodrigues J, Sorger PK, Laffenburger DA..셀 시그널링 네트워크 분석을 위한 논리 기반 모델.생화학(2010) 49(15) : 3216–24.10.1021/bi902202q
- ^ Helikar T, Kowal B, Madrahimov A, Shresta M, Pedersen J, Limbu K 등Bio-Logic Builder: 역동적이고 질적인 모델을 구축하기 위한 비기술적인 도구입니다.PLoS One (2012) 7(10): e46417.10.1371/journal.pone.0046417
- ^ http://covertlab.stanford.edu/publicationpdfs/mgenitalium_whole_cell_2012_07_20.pdf[영구 데드링크]
- ^ "Stanford researchers produce first complete computer model of an organism". 2012-07-19.
- ^ Gérard, Claude; Tyson, John J.; Coudreuse, Damien; Novák, Béla (2015-02-06). "Cell Cycle Control by a Minimal Cdk Network". PLOS Comput Biol. 11 (2): e1004056. Bibcode:2015PLSCB..11E4056G. doi:10.1371/journal.pcbi.1004056. PMC 4319789. PMID 25658582.
- ^ Gershon, Diane (2002). "Silicon dreams in the biology lab". Nature. 417 (6892): 4–5. Bibcode:2002Natur.417....4G. doi:10.1038/nj6892-04a. PMID 12087360. S2CID 10737442.