MicroRNA 시퀀싱
MicroRNA sequencingMicroRNA sequencing (miRNA-seq), a type of RNA-Seq, is the use of next-generation sequencing or massively parallel high-throughput DNA sequencing to sequence microRNAs, also called miRNAs. miRNA-seq differs from other forms of RNA-seq in that input material is often enriched for small RNAs. miRNA-seq allows researchers to examine tissue-specific exmiRNA의 pression pattern, 질병 연관성 및 isoforms, 그리고 이전에 특성화되지 않았던 miRNA를 발견하기 위해.잘못 조절된 miRNA가 암과[1] 같은 질병에서 역할을 한다는 증거는 miRNA-seq가 향후 비용이 계속 감소함에 따라 진단과 예후를 위한 중요한 도구가 될 가능성이 있는 위치를 잡았다.[2]다른 miRNA 프로파일링 기술과 마찬가지로 miRNA-Seq는 장점(순차 독립성, 적용 범위)과 단점(고비용, 인프라 요구사항, 실행 길이, 잠재적 아티팩트)을 모두 가지고 있다.[3]null
소개
마이크로RNA(microRNAs)는 길이가 21~25개의 뉴클레오티드인 작은 리보핵산 계열로, 성적 저하, 번역 억제, 성적서 격리 등을 통해 단백질 발현을 조절한다.[4][5][6]최초로 발견된 miRNA인 lin-4는 유전 돌연변이 유발 스크린에서 선충의 후발달을 제어하는 분자 원소를 식별하기 위해 발견되었다.[7]그 lin-4 유전자를lin-14 mRNAtranscript[8]의3'-untranslated 지역에서 여러분에게 보완적 구속력 있는 사이트들과 LIN-14 단백질 표현 downregulated 22뉴클레오티드 RNA를 인코딩했다.[9]miRNAs 지금 많은 생물학적 발육 프로세스의 조혈(Mus musculus[10]에 miR-181), 미스터리 한 등 규제에 관련된 것으로 생각된다.pid 대사(드로소필라 멜라노가스터의[11] miR-14)와 신경 발달(새너하브디트리스의[12] lsy-6)[6]이러한 발견은 miRNA-seq와 같은 miRNA를 식별하고 특성화할 수 있는 기술의 개발이 필요했다.null
역사
MicroRNA 시퀀싱(miRNA-seq)은 주어진 샘플에서 새로운 miRNA와 표현 프로파일을 찾기 위해 차세대 시퀀싱 또는 대규모 병렬 고투과 시퀀싱 기술을 활용하기 위해 개발되었다.miRNA 시퀀싱 자체는 새로운 아이디어가 아니며, Sanger 시퀀싱 메트호(Sequence methods. 염기서열 및 젤 전기생식으로 선택된 21–25 bp 크기의 내생성 소형 RNA에서 역코더한 DNA의 복제를 통해 라이브러리를 만드는 것이 순서 준비 작업에 포함되었다.[13]그러나 이 방법은 각 복제본을 개별적으로 증폭하고 시퀀싱 준비를 해야 하기 때문에 시간과 자원의 측면에서 철저하다.이 방법은 표현력이 높은 miRNA도 무심코 선호한다.[6]차세대 시퀀싱은 DNA 마이크로 어레이 분석에 필요한 시퀀스별 하이브리드화 탐침과 생어 시퀀싱 방법에 필요한 까다로운 복제 방법이 필요하지 않다.또한 miRNA-SEQ 방법의 차세대 시퀀싱 플랫폼은 단일 시퀀싱 실행으로 대형 소형 RNA 풀의 시퀀싱을 용이하게 한다.[14]null
miRNA-seq는 다양한 시퀀싱 플랫폼을 사용하여 수행할 수 있다.miRNA-seq 방법을 사용한 소형 RNA의 첫 번째 분석은 Lynx Therapeutics의 MPSS(Massive Parallel Signature Sequenceing) 시퀀싱 플랫폼을 사용하여 아라비도시스 탈리아나 모델 공장에서 약 140만 개의 소형 RNA를 검사했다.이 연구는 소형 RNA 연구를 위한 새로운 고투과 시퀀싱 기술의 가능성을 입증했고, 게놈은 식물을 특히 풍부한 소형 RNA 원천으로 하여 많은 수의 소형 RNA를 발생시킨다는 것을 보여주었다.[15]이후 연구에서는 새로운 18종의 miRNA 유전자와 21U-RNA라고 불리는 새로운 종류의 네마토드 소형 RNA를 식별한 씨엘레건 연구와 같은 다른 염기서열 기술을 사용했다.[16]인간의 자궁경부 종양과 정상 조직의 작은 RNA 프로필을 비교하는 또 다른 연구는 Illumina (회사) 게놈 분석기를 활용하여 64개의 새로운 인간 miRNA 유전자와 67개의 미RNA를 구별했다.[17]응용 바이오시스템s SOLiD 염기서열 분석 플랫폼도 인간 유방암 검출 시 miRNA의 예측가치를 조사하는 데 활용됐다.[18]null
방법들
소형 RNA 준비
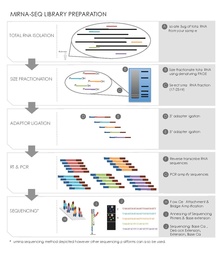
시퀀스 라이브러리 구축은 고용 중인 고투과 시퀀싱 플랫폼에 따라 다양한 키트를 사용하여 수행할 수 있다.그러나 작은 RNA 염기서열 작성에는 몇 가지 공통적인 단계가 있다.[19][20]null
총 RNA 절연
주어진 샘플에서 모든 RNA는 이소티오시아네이트/페놀/클로로포름(GITC/페놀) 방법 또는 트리졸(인비트로겐) 시약과 같은 상용 제품을 사용하여 추출 및 격리된다.시작량인 50-100μg 총 RNA, 조직 1g은 일반적으로 1mg의 총 RNA를 산출하는데 젤 정화와 크기 선택에 필요하다.[20]RNA의 품질 관리도 측정된다. 예를 들어, Caliper LabChipGX(Caliper Life Science)에서 RNA 칩을 구동한다.null
겔전기생식에 의한 소형 RNA의 크기분포함수
고립된 RNA는 변성성 폴리아크릴라미드 젤로 작동된다.크기 사다리와 함께 방사성 5'-32P 라벨이 부착된 올리고뉴클레오티드와 같은 영상 방법을 사용하여 적절한 크기의 RNA를 포함하는 젤의 단면을 식별함으로써 궁극적으로 배열되는 물질의 양을 줄인다.이 단계는 아래에 설명된 레그레이션 및 역전사 단계를 수행하기 전에 반드시 수행될 필요는 없다.[19][20]null
레그먼트
레인지 단계는 역전사 및 PCR 증폭 시 프라이머 결합 부위의 역할을 하는 소형 RNA의 양 끝에 DNA 어댑터를 추가한다.아데닐화 단일 가닥 DNA 3'adaptor에 이어 5'adaptor를 T4 RNA ligase2와 같은 묶는 효소를 사용하여 작은 RNA에 묶는다.또한 어댑터는 5' 히드록실 그룹을 가진 RNA 분해 제품이 아닌 5' 인산염 그룹, 특징적인 마이크로RNA로 작은 RNA를 포획하도록 설계되었다.[19][20]null
역전사 및 PCR 증폭
이 단계는 작은 어댑터 결합 RNA를 염기서열 반응에 사용되는 cDNA 클론으로 변환한다.이 단계를 어떤 형태로든 역성분화효소를 사용하여 수행할 수 있는 상용 키트가 많이 있다.그런 다음 PCR을 수행하여 cDNA 시퀀스 풀을 증폭한다.고유한 뉴클레오티드 태그로 설계된 프라이머를 이 단계에서 사용하여 풀링된 라이브러리 멀티플렉스 시퀀싱에서 ID 태그를 만들 수도 있다.[19][20]null
시퀀싱
실제 RNA 염기서열은 사용되는 플랫폼에 따라 크게 달라진다.세 가지 일반적인 차세대 시퀀싱[21] 플랫폼은 454 Life Science 플랫폼에서 파이로시퀀싱,[22] Illumina(회사) 플랫폼에서 폴리머아제 기반 시퀀스 바이합성 또는 ABI 솔리드 시퀀싱 플랫폼에서 레깅에 의한 시퀀싱이다.[23][24]null
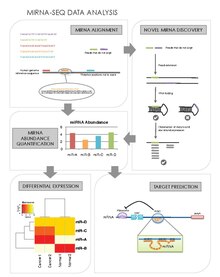
데이터 분석
miRNA-seq 데이터 분석의 중심은 1) 시퀀스 읽기로부터 miRNA 풍부 수준을 얻는 능력, 2) 참신한 miRNA를 발견하여 3) 차등표현 miRNA 및 관련 mRNA 유전자 대상을 결정할 수 있는 능력이다.null
miRNA 정렬 및 풍부함 수량화
miRNA는 특정 세포 유형, 조직, 발달 단계 또는 암과 같은 특정 질병 상태로 우선적으로 표현될 수 있다.[1]이후 딥 시퀀싱(miRNA-seq)샘플에서 읽기에 재미 있을 수백만명의를 생성할 때 우리;그것이 그들의 절대적인 풍요를 수량화가 있지만, 그들의 변형(isomirs[25]으로 알려져)을 발견하기 위해 miRNAs서 프로파일링 할 수 있습니다.참고가 순차 읽기의 평균 길이는 평균 miRNA(17-25 nt)보다, 3', 월의 5끝 길다.e miRNA는 동일한 판독값에서 찾을 수 있어야 한다.몇 가지 miRNA 풍부 계량 알고리즘이 있다.[21][26]이들의 일반적인 단계는 다음과 같다.[27]
- 시퀀싱 후 원시 시퀀스 판독값을 품질에 따라 필터링한다.어댑터 시퀀스도 원시 시퀀스 판독값에서 잘라낸다.
- 그런 다음, 결과 판독치는 각 고유 태그에 대해 복사 번호와 시퀀스가 기록되는 fasta 파일로 포맷된다.
- E를 나타낼 수 있는 시퀀스대장균 오염은 E에 대한 블라스트 검색으로 확인된다.대장균 데이터베이스는 분석에서 제거된다.
- 나머지 각 시퀀스는 miRNA 시퀀스 데이터베이스(miRBase[28] 등)에 맞춰 정렬됨 불완전한 DICER 처리를 설명하기 위해 3의 끝에서 6nt 오버행, 5의 끝에서 3nt 오버행이 허용된다.
- 그런 다음 miRNA 데이터베이스에 맞지 않는 읽기는 돌연변이를 일으킬 수 있는 miRNA 또는 RNA 편집을 거친 miRNA를 탐지하기 위해 miRNA 전구체에 느슨하게 정렬된다.
- 그런 다음 각 miRNA에 대한 읽기 횟수를 매핑된 총 miRNA 수로 정규화하여 각 miRNA의 풍부함을 보고한다.
참신한 miRNA 디스커버리
miRNA-seq의 또 다른 장점은 전통적인 선별과 프로파일링 방법을 피할 수 있는 새로운 miRNA의 발견을 허용한다는 것이다.[27]몇 가지 새로운 miRNA 발견 알고리즘이 있다.이들의 일반적인 단계는 다음과 같다.
- 알려진 miRNA 시퀀스에 맞지 않는 읽기를 얻어 게놈에 매핑한다.
- RNA접기법
- miRNA 시퀀스가 정확히 일치했으므로 양쪽 측면의 플랭킹 시퀀스 ~100bp를 포함한 게놈 시퀀스를 구하고, 빈 패키지 등의 RNA 폴딩 소프트웨어를 통해 RNA를 실행한다.[29]
- miRNA 헤어핀의 한쪽 팔에 놓여 있고 최소 자유 에너지가 ~25kcal/mol 미만인 접힌 시퀀스는 putative miRNA로 최종 등재된다.
- 열거된 순서는 가능한 전구순서만 포함하도록 잘라낸 다음 인접순서에 의해 전구가 인위적으로 안정화되지 않았는지 확인하기 위해 다시 판매한다.
- 결과적으로 접힌 순서는 miRNA 순서가 머리핀의 한쪽 팔 안에 들어가면 새로운 miRNA로 간주되며, 종들 간에 보존성이 높다.
- 별 Strand 표현 방법(miR딥[30])
- 새로운 miRNA 시퀀스는 DICER 프로세싱으로 인해 표시되는 특성 표현 패턴, 즉 항성 스트랜드 및 루프 시퀀스 위에 성숙한 miRNA를 더 높게 표현하여 식별한다.
차등식 분석
각 표본에 대해 miRNA의 함수를 정량화한 후, 표본 간에 miRNA의 표현 수준을 비교할 수 있다.그런 다음 특정 시점 또는 특정 조직이나 질병 상태를 우선적으로 나타내는 miRNA를 식별할 수 있을 것이다.샘플 간 매핑된 읽기 수에 대해 정규화한 후, 유전자 표현 프로파일링에 사용되는 것과 같은 통계적 테스트의 호스트를 사용하여 차등 표현을 결정할 수 있다.
대상 예측
miRNA의 mRNA 표적들을 식별하는 것은 그들이 발현을 조절하는 유전자의 유전자나 네트워크에 대한 이해를 제공할 것이다.[31]공공 데이터베이스는 miRNA 대상의 예측을 제공한다.그러나 진정한 긍정 예측과 잘못된 긍정 예측을 더 잘 구별하기 위해 miRNA-seq 데이터를 mRNA-seq 데이터에 통합하여 miRNA:mRNA 기능 쌍을 관찰할 수 있다.RNA22,[32] TargetScan,[33][34][35][36][37][38] miRanda,[39] PicTar는[40] 이러한 목적을 위해 설계된 소프트웨어다.예측 소프트웨어 목록이 여기에 제시되어 있다.일반적인 단계는 다음과 같다.
- mRNA:mRNA 바인딩 쌍을 결정하며, mRNA 시퀀스의 3'-UTR에서 miRNA 시퀀스 사이의 상호보완성이 확인된다.
- 종 간에 miRNA:mRNA 바인딩 쌍의 보존 정도를 결정한다.일반적으로 결합력이 높은 쌍은 예측의 잘못된 긍정이 될 가능성이 적다.
- mRNA-seq 또는 단백질 표현 데이터에서 miRNA를 대상으로 한 증거가 있는지 관찰하십시오. miRNA 발현이 높은 경우 대상 유전자의 유전자와 단백질 발현이 낮아야 한다.
절삭된 mRNA 대상에 대한 대상 유효성 검사
많은 miRNA는 그들의 mRNA 목표의 분리를 지시하는 기능을 한다. 이것은 특히 식물에서 사실이다. 따라서 고투입 시퀀싱 방법은 분해되거나 분해된 mRNA의 미개봉 3의 끝을 시퀀싱함으로써 miRNA의 이 특성을 이용하도록 개발되었다.이러한 방법은 디그라돔 시퀀싱 또는 PARE로 알려져 있다.[41][42]특정 mRNA에서 표적 갈라짐의 유효성 검사는 일반적으로 유전자 특정 프라이머로 cDNA Ends의 5' Rapid Amplification 버전을 사용하여 수행된다.null
적용들
새로운 miRNA의 식별
miRNA-seq는 기존의 miRNA 프로파일링 방식에서 벗어난 새로운 miRNA를 공개했다.그러한 발견의 예로는 배아줄기세포,[25] 닭 배아,[43] 급성 림프성 백혈병,[44] 확산성 b세포 림프종과 b세포,[45] 급성 골수성 백혈병,[46] 폐암 등이 있다.[47]null
질병 바이오마커
마이크로 RNA는 생존, 증식, 분화와 같은 거의 모든 세포 과정의 중요한 조절장치다.결과적으로, miRNA가 온코와 종양 억제기 유전자 발현에 대한 규제를 통해 암의 다양한 측면에 관여하는 것은 예상 밖의 일이 아니다.고투과 프로파일링 방법의 개발과 결합하여 miRNA는 암 분류, 치료에 대한 대응, 예후 등을 위한 바이오마커로 확인되었다.[48]또한 miRNA는 유전자 발현을 규제하기 때문에 특정 장애를 일으킬 수 있는 중요한 규제 네트워크에서 동요를 나타낼 수도 있다.[48]miRNA를 바이오마커로, 질병의 예측자로 몇 가지 적용이 아래에 제시되어 있다.null
| 암종류 | miRNAs α | 참조 |
|---|---|---|
| 유방 | ||
| ER 상태 | miR-26a/b, miR-30 패밀리, miR-29b, miR-155, miR-342, miR-206, miR-191 | [49][50][51][52] |
| PR 상태 | let-7c, miR-29b, miR-26a, miR-30 패밀리, miR-520g | [52][53] |
| HER2/neu 상태 | miR-520d, miR-181c, miR-302c, miR-376b, miR-30e | [49][53] |
| 폐 | ||
| 편평 셀 대 비 편평 셀 | miR-205 | [54] |
| 소세포 vs 비소세포 | miR-17-5p, miR-22, miR-24, miR-31 | [48] |
| 위 | ||
| 확산 vs 장 | miR-29b/c, miR-30 패밀리, miR-135a/b | [55] |
| 자궁내막 | ||
| 자궁내막 vs 자궁내막 | miR-19a/b, miR-30e-5p, miR-101, miR-452, miR-382, miR-15a, miR-29c | [56] |
| 레날 | ||
| 투명한 세포 vs 유두 | miR-424, miR-203, miR-31, miR-126 | [57] |
| 온코시토마 vs 크로모포베 | miR-200c, miR-139-5p | [57] |
| 골수종 | ||
| t(14;16)과 함께 | miR-1, miR-133a | [58] |
| t(4;14)와 함께 | miR-203, miR-155, miR-375 | [58] |
| t(11;14)와 함께 | miR-125a, miR-650, miR-184 | [58] |
| 급성 골수성 백혈병 | ||
| t(15;17)와 함께 | miR-382, miR-134, miR-376a, miR-127, miR-299-5p, miR-323 | [59] |
| t(8;21) 또는 inv(16)와 함께 | let-7b/c, miR-127 | [59] |
| NPM1 돌연변이로 | miR-10a/b, let-7, miR-29, miR-204, miR-128a, miR-196a/b | [59][60] |
| FLT3 ITD로 | miR-155 | [59][60][61] |
| 만성 림프구 백혈병 | ||
| ZAP-70 수준 및 IgVH 상태 | miR-15a, miR-195, miR-221, miR-155, miR-23b | [62] |
| 흑색종 | ||
| BRAF V600E와 함께 | miR-193a, miR-338, miR-565 | [63] |
| 림프종 | ||
| 확산 Large B세포 림프종 | has-miR-128, has-miR-129-3p, has-miR-152, has-miR-155, has-miR-185, has-miR-193a-5p, has-miR-196b, has-miR-199b-3p, has-miR-20b, has-miR-23a, has-miR-27a, has-miR-28-5p, has-miR-301a, has-miR-331-3p, has-miR-365, has-miR-625, has-miR-9 | [45] |
α이것은 이러한 악성종양과 관련된 miRNA의 포괄적인 목록이 아니다.null
miRNA 프로파일링의 다른 방법과 비교
miRNA 프로파일링의 다른 방법보다 miRNA-seq를 사용할 때의 단점은 miRNA-seq가 더 비싸고, 일반적으로 총 RNA의 양이 더 많이 필요하며, 광범위한 증폭을 수반하며, 마이크로 어레이 및 QPCR 방법보다 시간이 더 많이 소요된다는 것이다.[3]또한 miRNA-seq 라이브러리 준비 방법은 miRNA 보완을 체계적으로 우선시하는 것으로 보이며, 이는 miRNA 풍부성의 정확한 판단을 방해한다.[64]동시에 접근방식은 혼합 독립적이므로 선행 시퀀스 정보가 필요하지 않다.이 때문에 참신한 miRNA와 miRNA 이소폼(isoMirs)의 시퀀스를 얻을 수 있고, 순차적으로 유사한 miRNA를 구별할 수 있으며, 포인트 변이를 확인할 수 있다.[65]null
miRNA 프로파일링의 플랫폼 비교
| qPCR | 마이크로어레이 | 시퀀싱 | |
|---|---|---|---|
| 처리 시간 | ~6시간 | ~2일 | 1-2주 |
| 필요한 총 RNA | 500 ng | 100-1,000 ng | 500-5,000 ng |
| 동적 범위가 감지됨 | 진도 6개 | 진도 4개 | 5개 이상의 크기 순서 |
| 인프라 및 기술 요구사항 | 적다 | 중간 | 실속 있는 |
| 샘플당 비용(USD) | $400 | $250–$350 | $500–$700 |
참조
- ^ a b Farazi, Thalia A; Spitzer, Jessica I; Morozov, Pavel; Tuschl, Thomas (2011). "miRNAs in human cancer". The Journal of Pathology. 223 (2): 102–115. doi:10.1002/path.2806. ISSN 0022-3417. PMC 3069496. PMID 21125669.
- ^ Sandhu, S.; Garzon, R. (2011). "Potential Applications of MicroRNAs in Cancer Diagnosis, Prognosis, and Treatment". Semin Oncol. 38 (6): 781–787. doi:10.1053/j.seminoncol.2011.08.007. PMID 22082764.
- ^ a b c Baker, Monya (2010). "MicroRNA profiling: separating signal from noise". Nature Methods. 7 (9): 687–692. doi:10.1038/nmeth0910-687. ISSN 1548-7091. PMID 20805796. S2CID 6853222.
- ^ Kim, V. Narry; Han, Jinju; Siomi, Mikiko C. (2009). "Biogenesis of small RNAs in animals". Nature Reviews Molecular Cell Biology. 10 (2): 126–139. doi:10.1038/nrm2632. ISSN 1471-0072. PMID 19165215. S2CID 8360619.
- ^ Bartel, D (2004). "MicroRNAsGenomics, Biogenesis, Mechanism, and Function". Cell. 116 (2): 281–297. doi:10.1016/S0092-8674(04)00045-5. ISSN 0092-8674. PMID 14744438. S2CID 2669459.
- ^ a b c He, Lin; Hannon, Gregory J. (2004). "MicroRNAs: small RNAs with a big role in gene regulation". Nature Reviews Genetics. 5 (7): 522–531. doi:10.1038/nrg1379. ISSN 1471-0056. PMID 15211354. S2CID 86602746.
- ^ Ambros, Victor (1989). "A hierarchy of regulatory genes controls a larva-to-adult developmental switch in C. elegans". Cell. 57 (1): 49–57. doi:10.1016/0092-8674(89)90171-2. ISSN 0092-8674. PMID 2702689. S2CID 13103224.
- ^ Lee, Rosalind C.; Feinbaum, Rhonda L.; Ambros, Victor (1993). "The C. elegans heterochronic gene lin-4 encodes small RNAs with antisense complementarity to lin-14". Cell. 75 (5): 843–854. doi:10.1016/0092-8674(93)90529-Y. ISSN 0092-8674. PMID 8252621.
- ^ Wightman, Bruce; Ha, Ilho; Ruvkun, Gary (1993). "Posttranscriptional regulation of the heterochronic gene lin-14 by lin-4 mediates temporal pattern formation in C. elegans". Cell. 75 (5): 855–862. doi:10.1016/0092-8674(93)90530-4. ISSN 0092-8674. PMID 8252622.
- ^ Chen, C.-Z. (2004). "MicroRNAs Modulate Hematopoietic Lineage Differentiation" (PDF). Science. 303 (5654): 83–86. Bibcode:2004Sci...303...83C. doi:10.1126/science.1091903. hdl:1721.1/7483. ISSN 0036-8075. PMID 14657504. S2CID 7044929.
- ^ Xu, Peizhang; Vernooy, Stephanie Y.; Guo, Ming; Hay, Bruce A. (2003). "The Drosophila MicroRNA Mir-14 Suppresses Cell Death and Is Required for Normal Fat Metabolism" (PDF). Current Biology. 13 (9): 790–795. doi:10.1016/S0960-9822(03)00250-1. ISSN 0960-9822. PMID 12725740. S2CID 6391484.
- ^ Johnston, Robert J.; Hobert, Oliver (2003). "A microRNA controlling left/right neuronal asymmetry in Caenorhabditis elegans". Nature. 426 (6968): 845–849. Bibcode:2003Natur.426..845J. doi:10.1038/nature02255. ISSN 0028-0836. PMID 14685240. S2CID 4410288.
- ^ Lee, R. C. (2001). "An Extensive Class of Small RNAs in Caenorhabditis elegans". Science. 294 (5543): 862–864. Bibcode:2001Sci...294..862L. doi:10.1126/science.1065329. ISSN 0036-8075. PMID 11679672. S2CID 33480585.
- ^ Aldridge, Sarah; Hadfield, James (2012). Introduction to miRNA Profiling Technologies and Cross-Platform Comparison. Methods in Molecular Biology. Vol. 822. Next-Generation MicroRNA Expression Profiling Technology. pp. 19–31. doi:10.1007/978-1-61779-427-8_2. ISBN 978-1-61779-426-1. ISSN 1064-3745. PMID 22144189.
- ^ Lu, C; Tej, SS; Luo, S; Haudenschild, CD; Meyers, BC; Green, PJ (Sep 2, 2005). "Elucidation of the small RNA component of the transcriptome". Science. 309 (5740): 1567–9. Bibcode:2005Sci...309.1567L. doi:10.1126/science.1114112. PMID 16141074. S2CID 1651848.
- ^ Ruby, J. Graham; Jan, Calvin; Player, Christopher; Axtell, Michael J.; Lee, William; Nusbaum, Chad; Ge, Hui; Bartel, David P. (2006). "Large-Scale Sequencing Reveals 21U-RNAs and Additional MicroRNAs and Endogenous siRNAs in C. elegans". Cell. 127 (6): 1193–1207. doi:10.1016/j.cell.2006.10.040. ISSN 0092-8674. PMID 17174894. S2CID 16838469.
- ^ Witten, Daniela; Tibshirani, Robert; Gu, Sam; Fire, Andrew; Lui, Weng-Onn (2010). "Ultra-high throughput sequencing-based small RNA discovery and discrete statistical biomarker analysis in a collection of cervical tumours and matched controls". BMC Biology. 8 (1): 58. doi:10.1186/1741-7007-8-58. ISSN 1741-7007. PMC 2880020. PMID 20459774.
- ^ Wu, Qian; Lu, Zuhong; Li, Hailing; Lu, Jiafeng; Guo, Li; Ge, Qinyu (2011). "Next-Generation Sequencing of MicroRNAs for Breast Cancer Detection". Journal of Biomedicine and Biotechnology. 2011: 1–7. doi:10.1155/2011/597145. ISSN 1110-7243. PMC 3118289. PMID 21716661.
- ^ a b c d Lu, C; Meyers, BC; Green, PJ (October 2007). "Construction of small RNA cDNA libraries for deep sequencing". Methods. 43 (2): 110–7. doi:10.1016/j.ymeth.2007.05.002. PMID 17889797.
- ^ a b c d e Hafner, Markus; Landgraf, Pablo; Ludwig, Janos; Rice, Amanda; Ojo, Tolulope; Lin, Carolina; Holoch, Daniel; Lim, Cindy; Tuschl, Thomas (2008). "Identification of microRNAs and other small regulatory RNAs using cDNA library sequencing". Methods. 44 (1): 3–12. doi:10.1016/j.ymeth.2007.09.009. ISSN 1046-2023. PMC 2847350. PMID 18158127.
- ^ a b Shendure, Jay; Ji, Hanlee (2008). "Next-generation DNA sequencing". Nature Biotechnology. 26 (10): 1135–1145. doi:10.1038/nbt1486. ISSN 1087-0156. PMID 18846087. S2CID 6384349.
- ^ "Archived copy". Archived from the original on 2011-05-26. Retrieved 2012-03-01.
{{cite web}}: CS1 maint: 타이틀로 보관된 사본(링크) - ^ "Illumina DesignStudio".
- ^ "Archived copy". Archived from the original on 2008-05-16. Retrieved 2008-05-16.
{{cite web}}: CS1 maint: 타이틀로 보관된 사본(링크) - ^ a b Morin, R. D.; O'Connor, M. D.; Griffith, M.; Kuchenbauer, F.; Delaney, A.; Prabhu, A.-L.; Zhao, Y.; McDonald, H.; Zeng, T.; Hirst, M.; Eaves, C. J.; Marra, M. A. (2008). "Application of massively parallel sequencing to microRNA profiling and discovery in human embryonic stem cells". Genome Research. 18 (4): 610–621. doi:10.1101/gr.7179508. ISSN 1088-9051. PMC 2279248. PMID 18285502.
- ^ Berninger, Philipp; Gaidatzis, Dimos; van Nimwegen, Erik; Zavolan, Mihaela (2008). "Computational analysis of small RNA cloning data". Methods. 44 (1): 13–21. doi:10.1016/j.ymeth.2007.10.002. ISSN 1046-2023. PMID 18158128.
- ^ a b Creighton, C. J.; Reid, J. G.; Gunaratne, P. H. (2009). "Expression profiling of microRNAs by deep sequencing". Briefings in Bioinformatics. 10 (5): 490–497. doi:10.1093/bib/bbp019. ISSN 1467-5463. PMC 2733187. PMID 19332473.
- ^ Kozomara, A.; Griffiths-Jones, S. (2010). "miRBase: integrating microRNA annotation and deep-sequencing data". Nucleic Acids Research. 39 (Database): D152–D157. doi:10.1093/nar/gkq1027. ISSN 0305-1048. PMC 3013655. PMID 21037258.
- ^ Hofacker, I. L.; Fontana, W.; Stadler, P. F.; Bonhoeffer, L. S.; Tacker, M.; Schuster, P. (1994). "Fast folding and comparison of RNA secondary structures". Monatshefte für Chemie. 125 (2): 167–188. doi:10.1007/BF00818163. ISSN 0026-9247. S2CID 19344304.
- ^ Yang, X.; Li, L. (2011). "miRDeep-P: a computational tool for analyzing the microRNA transcriptome in plants". Bioinformatics. 27 (18): 2614–5. doi:10.1093/bioinformatics/btr430. ISSN 1367-4803. PMID 21775303.
- ^ Cloonan, Nicole; Wani, Shivangi; Xu, Qinying; Gu, Jian; Lea, Kristi; Heater, Sheila; Barbacioru, Catalin; Steptoe, Anita L; Martin, Hilary C; Nourbakhsh, Ehsan; Krishnan, Keerthana; Gardiner, Brooke; Wang, Xiaohui; Nones, Katia; Steen, Jason A; Matigan, Nick; Wood, David L; Kassahn, Karin S; Waddell, Nic; Shepherd, Jill; Lee, Clarence; Ichikawa, Jeff; McKernan, Kevin; Bramlett, Kelli; Kuersten, Scott; Grimmond, Sean M (2011). "MicroRNAs and their isomiRs function cooperatively to target common biological pathways". Genome Biology. 12 (12): R126. doi:10.1186/gb-2011-12-12-r126. ISSN 1465-6906. PMC 3334621. PMID 22208850.
- ^ Miranda KC, Huynh T, Tay Y, Ang YS, Tam WL, Thomson AM, Lim B, Rigoutsos I (2006). "A pattern-based method for the identification of MicroRNA binding sites and their corresponding heteroduplexes". Cell. 126 (6): 1203–17. doi:10.1016/j.cell.2006.07.031. PMID 16990141. S2CID 12749133.
- ^ Lewis, BP; Burge CB; Bartel DP (Jan 14, 2005). "Conserved seed pairing, often flanked by adenosines, indicates that thousands of human genes are microRNA targets". Cell. 120 (1): 15–20. doi:10.1016/j.cell.2004.12.035. PMID 15652477. S2CID 17316349.
- ^ Grimson, A; Farh, KK; Johnston, WK; Garrett-Engele, P; Lim, LP; Bartel, DP (Jul 6, 2007). "MicroRNA targeting specificity in mammals: determinants beyond seed pairing". Molecular Cell. 27 (1): 91–105. doi:10.1016/j.molcel.2007.06.017. PMC 3800283. PMID 17612493.
- ^ Friedman, RC; Farh, KK; Burge, CB; Bartel, DP (January 2009). "Most mammalian mRNAs are conserved targets of microRNAs". Genome Research. 19 (1): 92–105. doi:10.1101/gr.082701.108. PMC 2612969. PMID 18955434.
- ^ Garcia, DM; Baek, D; Shin, C; Bell, GW; Grimson, A; Bartel, DP (Sep 11, 2011). "Weak seed-pairing stability and high target-site abundance decrease the proficiency of lsy-6 and other microRNAs". Nature Structural & Molecular Biology. 18 (10): 1139–46. doi:10.1038/nsmb.2115. PMC 3190056. PMID 21909094.
- ^ Agarwal, Vikram; Bell, George W.; Nam, Jin-Wu; Bartel, David P. (2015-08-12). "Predicting effective microRNA target sites in mammalian mRNAs". eLife. 4: e05005. doi:10.7554/eLife.05005. ISSN 2050-084X. PMC 4532895. PMID 26267216.
- ^ Agarwal, V; Subtelny, AO; Thiru, P; Ulitsky, I; Bartel, DP (4 October 2018). "Predicting microRNA targeting efficacy in Drosophila". Genome Biology. 19 (1): 152. doi:10.1186/s13059-018-1504-3. PMC 6172730. PMID 30286781.
- ^ Maziere, P; Enright, A (2007). "Prediction of microRNA targets". Drug Discovery Today. 12 (11–12): 452–458. doi:10.1016/j.drudis.2007.04.002. ISSN 1359-6446. PMID 17532529.
- ^ Krek, A.마이크로RNA 대상 식별.DAI-B 70/07, (2010).
- ^ German MA, Pillay M, Jeong DH, Hetawal A, Luo S, Janardhanan P, Kannan V, Rymarquis LA, Nobuta K, German R, De Paoli E, Lu C, Schroth G, Meyers BC, Green PJ (2008). "Global identification of microRNA-target RNA pairs by parallel analysis of RNA ends". Nat. Biotechnol. 26 (8): 941–946. doi:10.1038/nbt1417. PMID 18542052. S2CID 13187064.
- ^ Addo-Quaye C, Eshoo TW, Bartel DP, Axtell MJ (2008). "Endogenous siRNA and miRNA targets identified by sequencing of the Arabidopsis degradome". Curr. Biol. 18 (10): 758–762. doi:10.1016/j.cub.2008.04.042. PMC 2583427. PMID 18472421.
- ^ Buermans, Henk PJ; Ariyurek, Yavuz; van Ommen, Gertjan; den Dunnen, Johan T; 't Hoen, Peter AC (2010). "New methods for next generation sequencing based microRNA expression profiling". BMC Genomics. 11 (1): 716. doi:10.1186/1471-2164-11-716. ISSN 1471-2164. PMC 3022920. PMID 21171994.
- ^ Zhang, Baohong; Zhang, Hua; Yang, Jian-Hua; Zheng, Yu-Sheng; Zhang, Peng; Chen, Xiao; Wu, Jun; Xu, Ling; Luo, Xue-Qun; Ke, Zhi-Yong; Zhou, Hui; Qu, Liang-Hu; Chen, Yue-Qin (2009). "Genome-Wide Analysis of Small RNA and Novel MicroRNA Discovery in Human Acute Lymphoblastic Leukemia Based on Extensive Sequencing Approach". PLOS ONE. 4 (9): e6849. Bibcode:2009PLoSO...4.6849Z. doi:10.1371/journal.pone.0006849. ISSN 1932-6203. PMC 2731166. PMID 19724645.
- ^ a b Jima, D. D.; Zhang, J.; Jacobs, C.; Richards, K. L.; Dunphy, C. H.; Choi, W. W. L.; Yan Au, W.; Srivastava, G.; Czader, M. B.; Rizzieri, D. A.; Lagoo, A. S.; Lugar, P. L.; Mann, K. P.; Flowers, C. R.; Bernal-Mizrachi, L.; Naresh, K. N.; Evens, A. M.; Gordon, L. I.; Luftig, M.; Friedman, D. R.; Weinberg, J. B.; Thompson, M. A.; Gill, J. I.; Liu, Q.; How, T.; Grubor, V.; Gao, Y.; Patel, A.; Wu, H.; Zhu, J.; Blobe, G. C.; Lipsky, P. E.; Chadburn, A.; Dave, S. S. (2010). "Deep sequencing of the small RNA transcriptome of normal and malignant human B cells identifies hundreds of novel microRNAs". Blood. 116 (23): e118–e127. doi:10.1182/blood-2010-05-285403. ISSN 0006-4971. PMC 3012600. PMID 20733160.
- ^ Starczynowski, D. T.; Morin, R.; McPherson, A.; Lam, J.; Chari, R.; Wegrzyn, J.; Kuchenbauer, F.; Hirst, M.; Tohyama, K.; Humphries, R. K.; Lam, W. L.; Marra, M.; Karsan, A. (2010). "Genome-wide identification of human microRNAs located in leukemia-associated genomic alterations". Blood. 117 (2): 595–607. doi:10.1182/blood-2010-03-277012. ISSN 0006-4971. PMID 20962326.
- ^ Keller, Andreas; Backes, Christina; Leidinger, Petra; Kefer, Nathalie; Boisguerin, Valesca; Barbacioru, Catalin; Vogel, Britta; Matzas, Mark; Huwer, Hanno; Katus, Hugo A.; Stähler, Cord; Meder, Benjamin; Meese, Eckart (2011). "Next-generation sequencing identifies novel microRNAs in peripheral blood of lung cancer patients". Molecular BioSystems. 7 (12): 3187–99. doi:10.1039/c1mb05353a. ISSN 1742-206X. PMID 22027949.
- ^ a b c Chan, Elcie; Prado, Daniel Estévez; Weidhaas, Joanne Barnes (2011). "Cancer microRNAs: From subtype profiling to predictors of response to therapy". Trends in Molecular Medicine. 17 (5): 235–243. doi:10.1016/j.molmed.2011.01.008. ISSN 1471-4914. PMC 3092835. PMID 21354374.
- ^ a b Blenkiron, Cherie; Goldstein, Leonard D; Thorne, Natalie P; Spiteri, Inmaculada; Chin, Suet-Feung; Dunning, Mark J; Barbosa-Morais, Nuno L; Teschendorff, Andrew E; Green, Andrew R; Ellis, Ian O; Tavaré, Simon; Caldas, Carlos; Miska, Eric A (2007). "MicroRNA expression profiling of human breast cancer identifies new markers of tumor subtype". Genome Biology. 8 (10): R214. doi:10.1186/gb-2007-8-10-r214. ISSN 1465-6906. PMC 2246288. PMID 17922911.
- ^ Sempere, L. F.; Christensen, M.; Silahtaroglu, A.; Bak, M.; Heath, C. V.; Schwartz, G.; Wells, W.; Kauppinen, S.; Cole, C. N. (2007). "Altered MicroRNA Expression Confined to Specific Epithelial Cell Subpopulations in Breast Cancer". Cancer Research. 67 (24): 11612–11620. doi:10.1158/0008-5472.CAN-07-5019. ISSN 0008-5472. PMID 18089790.
- ^ Mattie, Michael D; Benz, Christopher C; Bowers, Jessica; Sensinger, Kelly; Wong, Linda; Scott, Gary K; Fedele, Vita; Ginzinger, David; Getts, Robert; Haqq, Chris (2006). "Optimized high-throughput microRNA expression profiling provides novel biomarker assessment of clinical prostate and breast cancer biopsies". Molecular Cancer. 5 (1): 24. doi:10.1186/1476-4598-5-24. ISSN 1476-4598. PMC 1563474. PMID 16784538.
- ^ a b Iorio, M. V.; Ferracin, M.; Liu, C.-G.; Veronese, A.; Spizzo, R.; Sabbioni, S.; Magri, E.; Pedriali, M.; Fabbri, M.; Campiglio, M.; Menard, S.; Palazzo, J. P.; Rosenberg, A.; Musiani, P.; Volinia, S.; Nenci, I.; Calin, G. A.; Querzoli, P.; Negrini, M.; Croce, C. M. (2005). "MicroRNA Gene Expression Deregulation in Human Breast Cancer". Cancer Research. 65 (16): 7065–7070. doi:10.1158/0008-5472.CAN-05-1783. ISSN 0008-5472. PMID 16103053.
- ^ a b Lowery, Aoife J; Miller, Nicola; Devaney, Amanda; McNeill, Roisin E; Davoren, Pamela A; Lemetre, Christophe; Benes, Vladimir; Schmidt, Sabine; Blake, Jonathon; Ball, Graham; Kerin, Michael J (2009). "MicroRNA signatures predict oestrogen receptor, progesterone receptor and HER2/neu receptor status in breast cancer". Breast Cancer Research. 11 (3): R27. doi:10.1186/bcr2257. ISSN 1465-5411. PMC 2716495. PMID 19432961.
- ^ Lebanony, D.; Benjamin, H.; Gilad, S.; Ezagouri, M.; Dov, A.; Ashkenazi, K.; Gefen, N.; Izraeli, S.; Rechavi, G.; Pass, H.; Nonaka, D.; Li, J.; Spector, Y.; Rosenfeld, N.; Chajut, A.; Cohen, D.; Aharonov, R.; Mansukhani, M. (2009). "Diagnostic Assay Based on hsa-miR-205 Expression Distinguishes Squamous From Nonsquamous Non-Small-Cell Lung Carcinoma". Journal of Clinical Oncology. 27 (12): 2030–2037. doi:10.1200/JCO.2008.19.4134. ISSN 0732-183X. PMID 19273703.
- ^ Ueda, Tetsuya; Volinia, Stefano; Okumura, Hiroshi; Shimizu, Masayoshi; Taccioli, Cristian; Rossi, Simona; Alder, Hansjuerg; Liu, Chang-gong; Oue, Naohide; Yasui, Wataru; Yoshida, Kazuhiro; Sasaki, Hiroki; Nomura, Sachiyo; Seto, Yasuyuki; Kaminishi, Michio; Calin, George A; Croce, Carlo M (2010). "Relation between microRNA expression and progression and prognosis of gastric cancer: a microRNA expression analysis". The Lancet Oncology. 11 (2): 136–146. doi:10.1016/S1470-2045(09)70343-2. ISSN 1470-2045. PMC 4299826. PMID 20022810.
- ^ Ratner, Elena S.; Tuck, David; Richter, Christine; Nallur, Sunitha; Patel, Rajeshvari M.; Schultz, Vince; Hui, Pei; Schwartz, Peter E.; Rutherford, Thomas J.; Weidhaas, Joanne B. (2010). "MicroRNA signatures differentiate uterine cancer tumor subtypes". Gynecologic Oncology. 118 (3): 251–257. doi:10.1016/j.ygyno.2010.05.010. ISSN 0090-8258. PMC 2918705. PMID 20542546.
- ^ a b Fridman, Eddie; Dotan, Zohar; Barshack, Iris; David, Miriam Ben; Dov, Avital; Tabak, Sarit; Zion, Orit; Benjamin, Sima; Benjamin, Hila; Kuker, Hagit; Avivi, Camila; Rosenblatt, Kinneret; Polak-Charcon, Sylvie; Ramon, Jacob; Rosenfeld, Nitzan; Spector, Yael (2010). "Accurate Molecular Classification of Renal Tumors Using MicroRNA Expression". The Journal of Molecular Diagnostics. 12 (5): 687–696. doi:10.2353/jmoldx.2010.090187. ISSN 1525-1578. PMC 2928434. PMID 20595629.
- ^ a b c Gutiérrez, N C; Sarasquete, M E; Misiewicz-Krzeminska, I; Delgado, M; De Las Rivas, J; Ticona, F V; Fermiñán, E; Martín-Jiménez, P; Chillón, C; Risueño, A; Hernández, J M; García-Sanz, R; González, M; San Miguel, J F (2010). "Deregulation of microRNA expression in the different genetic subtypes of multiple myeloma and correlation with gene expression profiling". Leukemia. 24 (3): 629–637. doi:10.1038/leu.2009.274. ISSN 0887-6924. PMID 20054351.
- ^ a b c d Jongen-Lavrencic, M.; Sun, S. M.; Dijkstra, M. K.; Valk, P. J. M.; Lowenberg, B. (2008). "MicroRNA expression profiling in relation to the genetic heterogeneity of acute myeloid leukemia". Blood. 111 (10): 5078–5085. doi:10.1182/blood-2008-01-133355. ISSN 0006-4971. PMID 18337557.
- ^ a b Garzon, R.; Garofalo, M.; Martelli, M. P.; Briesewitz, R.; Wang, L.; Fernandez-Cymering, C.; Volinia, S.; Liu, C.-G.; Schnittger, S.; Haferlach, T.; Liso, A.; Diverio, D.; Mancini, M.; Meloni, G.; Foa, R.; Martelli, M. F.; Mecucci, C.; Croce, C. M.; Falini, B. (2008). "Distinctive microRNA signature of acute myeloid leukemia bearing cytoplasmic mutated nucleophosmin". Proceedings of the National Academy of Sciences. 105 (10): 3945–3950. Bibcode:2008PNAS..105.3945G. doi:10.1073/pnas.0800135105. ISSN 0027-8424. PMC 2268779. PMID 18308931.
- ^ Marcucci, Guido; Radmacher, Michael D.; Maharry, Kati; Mrózek, Krzysztof; Ruppert, Amy S.; Paschka, Peter; Vukosavljevic, Tamara; Whitman, Susan P.; Baldus, Claudia D.; Langer, Christian; Liu, Chang-Gong; Carroll, Andrew J.; Powell, Bayard L.; Garzon, Ramiro; Croce, Carlo M.; Kolitz, Jonathan E.; Caligiuri, Michael A.; Larson, Richard A.; Bloomfield, Clara D. (2008). "MicroRNA Expression in Cytogenetically Normal Acute Myeloid Leukemia". New England Journal of Medicine. 358 (18): 1919–1928. doi:10.1056/NEJMoa074256. ISSN 0028-4793. PMID 18450603.
- ^ Calin, George Adrian; Ferracin, Manuela; Cimmino, Amelia; Di Leva, Gianpiero; Shimizu, Masayoshi; Wojcik, Sylwia E.; Iorio, Marilena V.; Visone, Rosa; Sever, Nurettin Ilfer; Fabbri, Muller; Iuliano, Rodolfo; Palumbo, Tiziana; Pichiorri, Flavia; Roldo, Claudia; Garzon, Ramiro; Sevignani, Cinzia; Rassenti, Laura; Alder, Hansjuerg; Volinia, Stefano; Liu, Chang-gong; Kipps, Thomas J.; Negrini, Massimo; Croce, Carlo M. (2005). "A MicroRNA Signature Associated with Prognosis and Progression in Chronic Lymphocytic Leukemia". New England Journal of Medicine. 353 (17): 1793–1801. doi:10.1056/NEJMoa050995. ISSN 0028-4793. PMID 16251535.
- ^ Caramuta, Stefano; Egyházi, Suzanne; Rodolfo, Monica; Witten, Daniela; Hansson, Johan; Larsson, Catharina; Lui, Weng-Onn (2010). "MicroRNA Expression Profiles Associated with Mutational Status and Survival in Malignant Melanoma". Journal of Investigative Dermatology. 130 (8): 2062–2070. doi:10.1038/jid.2010.63. ISSN 0022-202X. PMID 20357817.
- ^ Linsen, Sam E V; de Wit, Elzo; Janssens, Georges; Heater, Sheila; Chapman, Laura; Parkin, Rachael K; Fritz, Brian; Wyman, Stacia K; de Bruijn, Ewart; Voest, Emile E; Kuersten, Scott; Tewari, Muneesh; Cuppen, Edwin (2009). "Limitations and possibilities of small RNA digital gene expression profiling". Nature Methods. 6 (7): 474–476. doi:10.1038/nmeth0709-474. ISSN 1548-7091. PMID 19564845. S2CID 7953265.
- ^ Git, A.; Dvinge, H.; Salmon-Divon, M.; Osborne, M.; Kutter, C.; Hadfield, J.; Bertone, P.; Caldas, C. (2010). "Systematic comparison of microarray profiling, real-time PCR, and next-generation sequencing technologies for measuring differential microRNA expression". RNA. 16 (5): 991–1006. doi:10.1261/rna.1947110. ISSN 1355-8382. PMC 2856892. PMID 20360395.